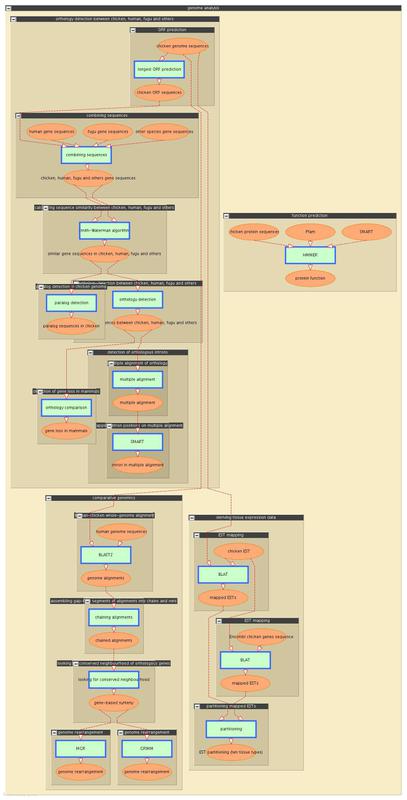
| 解析目的 | ゲノム解析 |
| Chicken_Workflow_1 |
| 解析目的 | 機能予測 |
| 入力データ | ニワトリタンパク質配列 |
| データベース | Pfam |
| データベース | SMART |
| 処理内容/ 解析ツール | HMMER |
| 処理条件 | ファミリーごとに特異的なカットオフ値を利用 |
| 出力データ | 機能予測結果 |
| Chicken_Workflow_2 |
| 解析目的 | ニワトリ・ヒト・フグ・その他ゲノム間のオーソログ同定 |
| Chicken_Workflow_2_1 |
| | 解析目的 | ORF予測 |
| | 入力データ | ニワトリゲノム配列 |
| | 処理内容/ 解析ツール | 最長ORF予測 |
| | 出力データ | ニワトリ最長ORF配列 |
| Chicken_Workflow_2_2 |
| | 解析目的 | 配列の結合 |
| | 入力データ | ニワトリ最長ORF配列 |
| | 入力データ | ヒト遺伝子配列 |
| | 入力データ | フグ遺伝子配列 |
| | 入力データ | その他生物種遺伝子配列 |
| | 処理内容/ 解析ツール | 配列の結合 |
| | 出力データ | ニワトリ・ヒト・フグ・その他遺伝子配列 |
| Chicken_Workflow_2_3 |
| | 解析目的 | ニワトリ・ヒト・フグ・その他遺伝子間の配列類似性計算 |
| | 入力データ | ニワトリ・ヒト・フグ・その他遺伝子配列 |
| | 入力データ | ニワトリ・ヒト・フグ・その他遺伝子配列 |
| | 処理内容/ 解析ツール | Smith-Watermanアルゴリズム |
| | 出力データ | ニワトリ・ヒト・フグ・その他間の類似遺伝子配列 |
| Chicken_Workflow_2_4 |
| | 解析目的 | ニワトリゲノムのパラログ同定 |
| | 入力データ | ニワトリ・ヒト・フグ間の類似遺伝子配列 |
| | 処理内容/ 解析ツール | パラログ同定 |
| | 処理条件 | 類似度の高い順にグループ化し、他のゲノムとの最大類似度まで繰り返す。20文字以上の重複 |
| | 出力データ | ニワトリゲノム内のパラログ配列 |
| Chicken_Workflow_2_5 |
| | 解析目的 | ニワトリ・ヒト・フグ・その他間のオーソログ同定 |
| | 入力データ | ニワトリ・ヒト・フグ・その他間の類似遺伝子配列 |
| | 処理内容/ 解析ツール | オーソログ同定 |
| | 処理条件 | 相互ベストヒットをもつ3タンパク質をグループ化し、20文字以上の重複をもつ限り類似度を下げる |
| | 出力データ | ニワトリ・ヒト・フグ・その他ゲノム間のオーソログ配列 |
| Chicken_Workflow_2_6 |
| | 解析目的 | 哺乳類の遺伝子喪失の同定 |
| | 入力データ | ニワトリ-ヒト-フグ・その他ゲノム間のオーソログ配列 |
| | 処理内容/ 解析ツール | 多生物種間のオーソログ比較 |
| | 処理条件 | 哺乳類との分岐以前に分岐した動物との間にオーソログ関係があるが、哺乳類との間にはない |
| | 出力データ | 哺乳類の喪失遺伝子 |
| Chicken_Workflow_2_7 |
| | 解析目的 | オーソロガスイントロンの同定 |
| | Chicken_Workflow_2_7_1 |
| | | 解析目的 | オーソログのマルチプルアライメント |
| | | 入力データ | ニワトリ-ヒト-フグ・その他ゲノム間のオーソログ配列 |
| | | 処理内容/ 解析ツール | マルチプルアライメント |
| | | 出力データ | マルチプルアライメント |
| | Chicken_Workflow_2_7_2 |
| | | 解析目的 | マルチプルアライメント上のイントロンマッピング |
| | | 入力データ | マルチプルアライメント |
| | | 処理内容/ 解析ツール | SMART |
| | | 出力データ | マルチプルアライメント上のイントロン |
| Chicken_Workflow_3 |
| 解析目的 | 組織別発現遺伝子の同定 |
| Chicken_Workflow_3_1 |
| | 解析目的 | ESTマッピング |
| | 入力データ | ニワトリゲノム配列 |
| | データベース | ニワトリESTデータ |
| | 処理内容/ 解析ツール | BLAT |
| | 処理条件 | 95%一致 |
| | 出力データ | ESTマッピング |
| Chicken_Workflow_3_2 |
| | 解析目的 | ESTマッピング |
| | 入力データ | Ensemblニワトリ遺伝子配列 |
| | データベース | ニワトリESTデータ |
| | 処理内容/ 解析ツール | BLAT |
| | 処理条件 | 95%一致 |
| | 出力データ | ESTマッピング |
| Chicken_Workflow_3_3 |
| | 解析目的 | ESTの組織別分類 |
| | 入力データ | ESTマッピング |
| | 入力データ | ESTマッピング |
| | 処理内容/ 解析ツール | 分類 |
| | 出力データ | EST分類(10組織別) |
| Chicken_Workflow_4 |
| 解析目的 | 比較ゲノム |
| Chicken_Workflow_4_1 |
| | 解析目的 | ヒト・ニワトリのホールゲノムアライメント |
| | 入力データ | ニワトリゲノム配列 |
| | データベース | ヒトゲノム配列 |
| | 処理内容/ 解析ツール | BLASTZ |
| | 出力データ | ゲノムアライメント |
| Chicken_Workflow_4_2 |
| | 解析目的 | ホールゲノムアライメントのチェイニング |
| | 入力データ | ゲノムアライメント |
| | 処理内容/ 解析ツール | アライメントのチェイニング |
| | 出力データ | ゲノムアライメントのチェイニング |
| Chicken_Workflow_4_3 |
| | 解析目的 | オーソログの保存並びの探索 |
| | 入力データ | ゲノムアライメントのチェイニング |
| | 処理内容/ 解析ツール | 保存された並びの探索 |
| | 出力データ | 遺伝子ベースのシンテニー領域 |
| Chicken_Workflow_4_4 |
| | 解析目的 | ゲノム再編成 |
| | 入力データ | 遺伝子ベースのシンテニー領域 |
| | 処理内容/ 解析ツール | MGR |
| | 出力データ | ゲノム再編成 |
| Chicken_Workflow_4_5 |
| | 解析目的 | ゲノム再編成 |
| | 入力データ | 遺伝子ベースのシンテニー領域 |
| | 処理内容/ 解析ツール | GRIMM |
| | 出力データ | ゲノム再編成 |